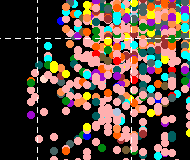
JBioFramework (JBF) es un conjunto de dos simulaciones de separaciones químicas diferentes (electroforesis 2D y espectrometría de masas) que se utilizan con frecuencia en la investigación en química, bioquímica y proteómica. Está escrito en el lenguaje de programación Java y se ejecutará en todos los sistemas que tengan instalada la JVM.
A medida que continuamos desarrollando el software en los próximos meses / años e intentamos cuantificar el éxito de nuestros esfuerzos con las pruebas y revisiones, la aportación de los usuarios es muy importante. No dude en revisar el software a continuación o envíe un correo electrónico a Paul Craig [pac8612@rit.edu] con descripciones más grandes / errores / ideas de funciones.
Nuestro próximo lanzamiento programado contendrá (además de 2DE y MassSpec) una simulación de electroforesis 1D, así como una pestaña que contiene MarvinSketch de ChemAxon [http://www.chemaxon.com/products/marvin/] junto con algunas funcionalidades mejoradas. Debería estar disponible en breve cuando completemos la creación y modificación de un dominio permanente para el proyecto.
Caracteristicas de JBioFramework:
- Simulación de electroforesis 2D completa con búsquedas de bases de datos específicas de proteínas
- Simulación de espectrómetro de masas integrada y modular.